Tausende von Proteinen im dunklen Proteom entdeckt
Die Gene in der DNA liefern den Bauplan, nach dem die Zellen miteinander verknüpfte Aminosäuren, die Peptide, herstellen. Bisher wurden Peptide immer dann als Proteine bezeichnet, wenn sie lang genug waren und es zudem Hinweise auf eine biologische Funktion gab – zum Beispiel weil das gleiche Molekül bei verschiedenen Arten und schon sehr lange in der Evolution existiert. Eine große internationale, kuratierte Proteindatenbank enthält derzeit rund 19.500 Einträge. Immer mehr Forschende sind allerdings der Ansicht, dass die traditionelle Definition eines Proteins erweitert werden muss – und es vermutlich noch viel mehr dieser Moleküle gibt.
Ein Team um Wissenschaftler*innen des Princess Máxima Center for Pediatric Oncology, der University of Michigan Medical School, des EMBL European Bioinformatics Institute und des Institute for Systems Biology hat jetzt mehr mehr als 7.200 bislang wenig erforschte DNA-Abschnitte untersucht, die als nicht-kanonische offene Leserahmen (non-canonical Open Reading Frames, kurz ncORFs) bezeichnet werden. Das Konsortium, zu dem auch Forschende des Max Delbrück Center gehören, fand heraus, dass etwa ein Viertel, fast 1.800, dieser Abschnitte, proteinähnliche Moleküle erzeugen. Diese sind kleiner als herkömmliche Proteine und werden daher als Mikroproteine bezeichnet. Veröffentlicht ist die Studie in der Fachzeitschrift „Nature“.
Blick in ein unbekanntes Universum
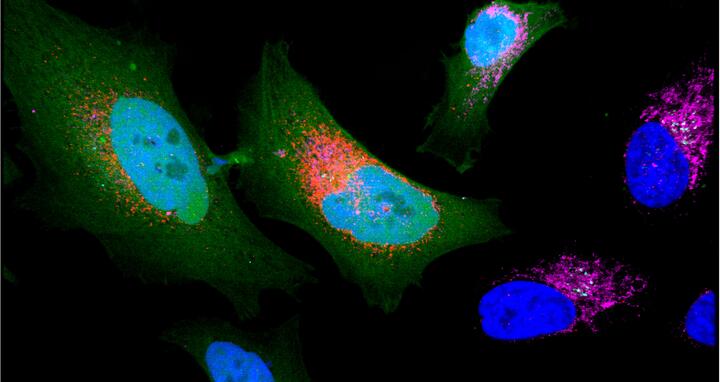
Mikroprotein, das von Krebszellen ausgeschüttet wird (rot).
Die Forschenden analysierten rund 3,7 Milliarden Rohdaten, die einen möglichen Hinweis auf bekannte und bisher unbekannte Proteine lieferten. Dabei stützten sie sich auf 95.520 Experimente, die mehrere Computer im Dauerbetrieb zusammen etwa 20.000 Stunden lang auswerteten. So identifizierte das Team 1.785 Mikroproteine – welche die Zahl der aktuell in der Datenbank gelisteten Proteine um fast 10 Prozent erhöhen würden.
Die meisten der 1.785 Mikroproteine unterscheiden sich von den rund 19.500 herkömmlichen Proteinen allerdings in vielerlei Hinsicht. Unter anderem sind sie sehr klein: 65 Prozent von ihnen bestehen aus weniger als 50 Aminosäuren. Von den bisher bekannten Proteinen haben nicht einmal ein Prozent eine solch geringe Größe. Bei genauerer Betrachtung der Mikroproteine stellten die Forschenden zudem fest, dass nur wenige von ihnen – vielleicht ein Dutzend – traditionellen Proteinen ähneln. Für den verbleibenden Großteil haben sie mehr als ein Jahr damit verbracht, um herauszufinden, wie man die Moleküle einordnen könnte.
Die Studie baut auf früheren Arbeiten eines Teams um Dr. Jorge Ruiz-Orera aus der Arbeitsgruppe „Genetik und Genomik von Herz-Kreislauferkrankungen“ von Professor Norbert Hübner am Max Delbrück Center auf. Hübners Labor hat das TransCODE Consortium, einen internationalen Zusammenschluss von mehr als 60 Forschenden aus über 30 Institutionen, mitgegründet und mitkoordiniert.
Gemeinsam mit der Arbeitsgruppe „Bioinformatik der Genregulation“ von Professor Uwe Ohler am Max Delbrück Center identifizierten die Wissenschaftler*innen um Ruiz-Orera mehr als 7.200 bisher kaum untersuchte ncORFs. Die Ergebnisse, die 2022 in „Nature Biotechnology“ veröffentlicht wurden, warfen grundlegende Fragen auf, die zur aktuellen Studie führten: Wie viele dieser Regionen produzieren stabile, proteinähnliche Moleküle, die im bekannten menschlichen Proteom nicht vorkommen? Wie viele davon haben eine biologische Funktion? Und kommen sie in der Evolution bei vielen Arten vor oder existieren sie allein beim Menschen?
Eine neue Sichtweise auf die DNA und ihre Proteine
Die Forschenden des TransCODE Consortium haben jetzt einen neuen biologischen Begriff geprägt: das Peptidein. Seit Jahrzehnten vertritt die wissenschaftliche Community eine binäre Sichtweise auf die Beziehung zwischen menschlicher DNA und menschlichen Proteinen. Ein bestimmter DNA-Abschnitt produziert demnach entweder ein Protein oder nicht. In ihrer neuen Studie schlagen die Wissenschaftler*innen eine dritte Option vor: Die DNA könnte den Baulan für ein Peptidein enthalten.
Das Team definiert ein Peptidein als ein in Zellen vorkommendes, proteinähnliches Molekül – was zunächst vor allem bedeutet, dass es wie Proteine aus Aminosäuren besteht. Die Rolle eines Peptideins ist jedoch unklar. Womöglich hat es in der menschlichen Biologie eine Funktion, vielleicht aber auch nicht. Das ist der wesentliche Unterschied zu herkömmlichen Proteinen, von denen man annimmt, dass sie alle eine Funktion besitzen, auch wenn deren Einzelheiten möglicherweise noch nicht vollständig bekannt sind.
Entscheidend ist, dass diese Definition eines Peptideins die Option offenlässt, das Molekül künftig als Protein zu definieren – vorausgesetzt, es liegen dann genügend Belege dafür vor. Um der Idee nachzugehen, suchte das Team nach Peptideinen, ohne die Zellen nicht überleben können. Diese pan-essenziellen Peptideine könnten wichtige Kandidaten für Wirkstoffziele bei Krebs und anderen Krankheiten sein.
Peptideine als Ziele für neue Medikamente
Mithilfe einer groß angelegten CRISPR-Geneditierung identifizierten die Wissenschaftler*innen sechs vielversprechende Peptideine. Eines davon war beispielsweise ein Molekül, das aus OLMALINC hergestellt wird – einer Gensequenz, von der man bisher annahm, dass sie keine Proteine produziert. Als die Forschenden das Gen ausschalteten, war die Überlebensfähigkeit bei 85 Prozent von gut 485 Krebszelllinien beeinträchtigt. Das Team konnte zeigen, dass dieser Effekt vom Peptidein selbst ausgeht und nicht von dem RNA-Molekül, auf das es zurückgeht. Zudem fanden die Wissenschaftler*innen heraus, dass das Peptidein eine Rolle bei der Zellteilung und der Reaktion auf DNA-Schäden spielt.
Viele der neu entdeckten Peptideine werden an der Zelloberfläche präsentiert, um vom Immunsystem erkannt zu werden, was sie zu potenziellen Zielen zum Beispiel bei der Krebsimmuntherapie macht. Vergleichbare Oberflächenmoleküle sind schon seit einiger Zeit als Wirkstoffziel in der Entwicklung. Und sowohl in der Wissenschaft als auch in der Industrie wächst das Interesse daran, diese neue Klasse von Krebsantigenen zu nutzen. Darüber hinaus könnten Peptideine Aufschluss über genetische Erkrankungen geben, die sich mit herkömmlichen Gentests bisher nicht diagnostizieren lassen – weil bis vor kurzem schlicht niemand wusste, dass das menschliche Genom die Moleküle kodiert.
Der Text beruht auf einer Pressemitteilung des Princess Máxima Center for Pediatric Oncology
Professor Norbert Hübner, Leiter der Arbeitsgruppe Genetik und Genomik von Herz-Kreislauferkrankungen am Max Delbrück Center, sagt:
„Wir stehen vor einer besonders spannenden Phase in der Biologie. Die Entdeckung von Hunderten von Peptideinen macht eine riesige und bislang übersehene Ebene des Genoms sichtbar und erweitert das bekannte Proteom erheblich. Das Verständnis ihrer Funktionen könnte die Art und Weise, wie wir menschliche Krankheiten, einschließlich Herz-Kreislauf-Erkrankungen, erforschen, grundlegend verändern und völlig neue therapeutische Möglichkeiten eröffnen.“
Dr. Sebastiaan van Heesch, Gruppenleiter am Princess Máxima Center for Pediatric Oncology, der die Studie mitgeleitet hat, sagt:
„Wir wissen, dass der derzeitige Überblick über bekannte Proteine nicht das gesamte Bild widerspiegelt. Mit dieser Studie zeigen wir, dass Tausende bisher übersehener genetischer Sequenzen zum dunklen Proteom beitragen – indem sie eine neue Klasse proteinähnlicher Moleküle, die Mikroproteine, produzieren, die bislang nicht erkannt worden waren. Bei den meisten von ihnen wissen wir allerdings noch nicht, welche Funktion sie haben.“
„Es war ein ganz besonderes Gefühl, darüber zu diskutieren und zu entscheiden, wie wir mit dieser neuen Molekülklasse verfahren sollten, da wir bereits genügend erste Hinweise darauf gesammelt hatten, dass sie möglicherweise in vielen Zelltypen und Geweben verbreitet sind. Indem wir diese Moleküle mit unbekannter Funktion als Peptideine klassifiziert haben, haben wir ihnen einen festen Platz in Referenzdatenbanken verschafft, sodass die breitere Forschungsgemeinschaft sie untersuchen kann.“
„Angesichts des wachsenden Interesses in Industrie und Wissenschaft stehen Peptideine im Mittelpunkt zahlreicher Initiativen zur Arzneimittelentwicklung. Ebenso spielen sie unserer Beobachtung nach eine immer wichtigere Rolle bei der Erforschung verschiedener Krankheiten, darunter auch Krebserkrankungen im Kindesalter. Wir hoffen, eine neue Forschungswelle zu Peptideinen anzustoßen und neue Erkenntnisse sowie neue Wirkstoffziele in der gesamten Humanbiologie zu erschließen, insbesondere für die Entwicklung von zellulären Immuntherapien und Krebsimpfstoffen.“
Professor John Prensner, Pädiatrischer Neuroonkologe der University of Michigan Medical School, der die Studie mitgeleitet hat, sagt:
„Wir fangen gerade erst an zu erkennen, was dieses dunkle Proteom zu bieten hat. Es ist wie der Trailer zu einem Film. Wir erahnen bereits die Umrisse einer bahnbrechenden Sichtweise auf die menschliche Biologie. Wir sind unglaublich gespannt darauf, welche neuen Wege die kommenden Jahre eröffnen werden, um menschliche Krankheiten wie Krebs zu erforschen und zu behandeln.“
Professor Robert Moritz, Gruppenleiter am Institute for Systems Biology, der die Studie mitgeleitet hat, sagt:
„Unsere gemeinsame Arbeit ist das Ergebnis jahrzehntelanger Investitionen staatlicher Förderorganisationen in den Aufbau der Rechen- und Dateninfrastruktur, die erforderlich war, um das Proteom am Institute for Systems Biology in einem wahrhaft beispiellosen Umfang zu untersuchen. Durch den Einsatz unserer praxiserprobten Trans Proteomic Pipeline bei fast 100.000 Massenspektrometrie-Experimenten, die 3,7 Milliarden Spektren umfassen – abgeleitet aus den weltweit öffentlich zugänglichen Massenspektrometrie-Daten, deren Ergebnisse im PeptideAtlas am ISB gespeichert sind, damit die wissenschaftliche Gemeinschaft sie einsehen und teilen kann – konnten wir mit hoher Sicherheit die Existenz von mehr als 1.700 dieser neu identifizierten Peptideine nachweisen, die der Wissenschaft andernfalls weitgehend verborgen geblieben wären.“
„Was mich am meisten begeistert, ist nicht einfach die Tatsache, dass diese Moleküle existieren, sondern was ihre Existenz bedeutet.“
„Die Biologie stützte sich lange Zeit auf eine relativ kleine Gruppe gut charakterisierter Proteine, um die Regulationslogik der Zelle zu erklären. Doch Peptideine deuten jetzt darauf hin, dass sich unter dieser vertrauten Ebene eine ganze bislang unerschlossene Schicht molekularer Akteure verbirgt, deren funktionelle Rolle bei der Genregulation, der Signalübertragung und beim Überleben der Zelle wir uns erst allmählich vorstellen können.
Angesichts ihrer geringeren Größe und der Vielfalt der zellulären Kontexte, in denen sie auftreten, glaube ich, dass sich Peptideine als einige der vielseitigsten und folgenreichsten regulatorischen Moleküle erweisen könnten, denen wir in der Humanbiologie bisher begegnet sind. Dies ist nicht das Ende einer Suche – es ist der Beginn eines weiten und fruchtbaren neuen Gebiets, das die gesamte wissenschaftliche Gemeinschaft erforschen und nutzen kann. Ich freue mich darauf, zu sehen, was die breitere Forschungscommunity aufdeckt, wenn diese Moleküle und viele weitere, deren Existenz noch bestätigt werden muss, ans Licht gebracht werden.“
Weitere Informationen
- Pressemitteilung des Princess Máxima Center for Pediatric Oncology (auf Englisch)
- Evolution: Miniproteine aus dem „Nichts“
- Stunde der unerforschten Gensegmente
- Zwei MDC-Wissenschaftler erhalten Millionenförderung vom Europäischen Forschungsrat ERC
Literatur
Eric W. Deutsch, Leron W. Kok, Jonathan M. Mudge, et al. (2026) „Expanding the human proteome with microproteins and peptideins“, Nature, DOI: doi.org/10.1038/s41586-026 – 10459‑x
- Über das TransCODE Consortium
Die Studie ist das Ergebnis des TransCODE Consortium, einer internationalen Kooperation von mehr als 60 Forschenden aus über 30 Einrichtungen weltweit, die gemeinsam vom Princess Máxima Center for Pediatric Oncology im niederländischen Utrecht, der University of Michigan Medical School, dem EMBL European Bioinformatics Institute in britischen Hinxton, dem Institute for Systems Biology in Seattle und dem Max Delbrück Center geleitet und koordiniert wird. Unterstützt haben die Arbeit unter anderem die US-amerikanischen National Institutes of Health, der National Science Foundation, der Oncode Accelerator (ein Programm des niederländischen National Growth Fund) und das Marie-Sklodowska-Curie-Programm der Europäischen Union.